Ribointerferencia
La ribointerferencia o RNAi (acrónimo del inglés RNA interference) es un sistema que utilizan las células de los organismos vivos para controlar los genes que están activos en un momento o un tipo celular, y su grado de activación. De forma más concreta, la ribointerferencia es un mecanismo de silenciamiento post-transcripcional de genes específicos, ejercido por moléculas de ARN que, siendo complementarias a un ARN mensajero, conducen habitualmente a la degradación de este.
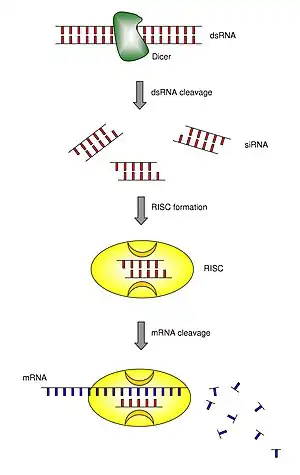
Debe distinguirse entre :
- Ribointerferencia (o interferencia por ARN, RNAi), que es el mecanismo biológico o la técnica experimental que lo aprovecha, y que presenta variaciones en función del tipo de molécula de ARN interferente implicada en el proceso.
- ARN interferente (en inglés, interfering RNA), que es la molécula de ARN que ejerce ribointerferencia, y puede ser de varios tipos (siRNA, miRNA o piRNA).
Evolución
A partir de estudios filogenéticos computacionales basados en el principio de máxima parsimonia, el ancestro común más reciente de todos los eucariotas probablemente ya poseía una ruta primitiva de RNAi; se piensa que la ausencia de la ruta en ciertos eucariotas es una característica derivada.[1] Este sistema de RNAi ancestral probablemente contenía una proteína similar a Dicer, una proteína Argonauta, una proteína PIWI, y una ARN polimerasa dependiente de ARN (RdRP) que podría haber realizado otras funciones celulares. Un estudio a gran escala de genómica comparativa también indica que el grupo corona (un grupo monofilético vivo, o clado, que consiste del último ascendente común de todos los ejemplares vivos, más todos sus descendientes) ya poseía estos componentes, que en aquel momento podrían haber tenido asociaciones funcionales más estrechas con los sistemas generales de degradación del ARN como el exosoma.[2] Este estudio también sugiere que la familia de proteínas "Argonauta" de unión a ARN, que es común entre los eucariotas, la mayoría de los Archaea, y al menos algunas bacterias (tales como Aquifex aeolicus), es homóloga y originalmente derivada de los componentes del sistema de iniciación de la traducción.
Se piensa que la función ancestral del sistema de RNAi es la defensa inmune contra elementos genéticos exógenos tales como transposones y genomas virales.[1][3] Algunas funciones relacionadas, como la modificación de histonas, podrían haber estado ya presentes en el ancestro de los modernos eucariotas, aunque parece que otras funciones como la regulación del desarrollo por los miRNA habrían aparecido posteriormente.[1]
Los genes de la ribointerferencia, como componentes del sistema inmune antiviral en muchos eucariotas, están implicados en una "batalla evolutiva" con los genes virales. Algunos virus han desarrollado mecanismos para suprimir la respuesta de RNAi de sus células huésped, un efecto muy aparente sobre todo en los virus de plantas.[4] Estudios de las tasas evolutivas en Drosophila muestran que los genes de la ruta de RNAi están sometidas una fuerte selección direccional y están entre los genes con una tasa de evolución más rápida del genoma de Drosophila.[5]
Algunos protozoos tales como Leishmania major y Trypanosoma cruzi carecen completamente de la ruta de RNAi.[6][7] La mayoría de los componentes también están ausentes en algunos hongos, notablemente en el organismo modelo Saccharomyces cerevisiae.[8] El hecho de que algunos ascomicetos y basidiomicetos carezcan de rutas de RNAi indica que algunas proteínas requeridas para la ribointerferencia se han perdido de forma independiente en muchos linajes de hongos, posiblemente debido a la evolución de una nueva ruta con función similar, o a la falta de ventaja selectiva en ciertos nichos.[9]
Véase también
Referencias
- Cerutti H, Casas-Mollano J (2006). «On the origin and functions of RNA-mediated silencing: from protists to man». Curr Genet 50 (2): 81-99. PMID 16691418. doi:10.1007/s00294-006-0078-x.
- Anantharaman V, Koonin E, Aravind L (2002). «Comparative genomics and evolution of proteins involved in RNA metabolism». Nucleic Acids Res 30 (7): 1427-64. PMID 11917006. doi:10.1093/nar/30.7.1427.
- Buchon N, Vaury C (2006). «RNAi: a defensive RNA-silencing against viruses and transposable elements». Heredity 96 (2): 195-202. PMID 16369574. doi:10.1038/sj.hdy.6800789.
- Lucy A, Guo H, Li W, Ding S (2000). «Suppression of post-transcriptional gene silencing by a plant viral protein localized in the nucleus». EMBO J 19 (7): 1672-80. PMID 10747034. doi:10.1093/emboj/19.7.1672.
- Obbard D, Jiggins F, Halligan D, Little T (2006). «Natural selection drives extremely rapid evolution in antiviral RNAi genes». Curr Biol 16 (6): 580-5. PMID 16546082. doi:10.1016/j.cub.2006.01.065.
- DaRocha W, Otsu K, Teixeira S, Donelson J (2004). «Tests of cytoplasmic RNA interference (RNAi) and construction of a tetracycline-inducible T7 promoter system in Trypanosoma cruzi». Mol Biochem Parasitol 133 (2): 175-86. PMID 14698430. doi:10.1016/j.molbiopara.2003.10.005.
- Robinson K, Beverley S (2003). «Improvements in transfection efficiency and tests of RNA interference (RNAi) approaches in the protozoan parasite Leishmania». Mol Biochem Parasitol 128 (2): 217-28. PMID 12742588. doi:10.1016/S0166-6851(03)00079-3.
- L. Aravind, Hidemi Watanabe, David J. Lipman, and Eugene V. Koonin (2000). «Lineage-specific loss and divergence of functionally linked genes in eukaryotes». Proceedings of the National Academy of Sciences 97 (21): 11319-11324. PMID 11016957. doi:10.1073/pnas.200346997.
- Nakayashiki H, Kadotani N, Mayama S (2006). «Evolution and diversification of RNA silencing proteins in fungi». J Mol Evol 63 (1): 127-35. PMID 16786437. doi:10.1007/s00239-005-0257-2.
- Claros G, Saladrigas V (2003): Vocabulario inglés-español de bioquímica y biología molecular (2.ª entrega) Panace@ IV (11): 18-29. Vocabulario completo en BioROM (enlace roto disponible en Internet Archive; véase el historial, la primera versión y la última)..
Enlaces externos
- Calvo JC (2003): Una nueva visión del ARN: los ARN de interferencia. ¿Un nuevo genoma? QuímicaViva 2(3). ISSN 1666-7948
- Kitabwalla M, Ruprecht RM (2002): RNA Interference — A New Weapon against HIV and Beyond N Engl J Med 347(17):1364-67. PMID 12397198